Es ist bekannt, dass sich das schwere akute respiratorische Syndrom, bekannt als COVID-19-Krankheit – verursacht durch das SARS-CoV-2-Virus – über Atemtröpfchen und enge Kontakte verbreitet.[1]Die Belastung durch COVID-19 war in der Lombardei und der Po-Ebene (Norditalien) äußerst hoch,[2] einem Gebiet, das durch hohe Feinstaubkonzentrationen gekennzeichnet ist, von denen bereits bekannt ist, dass sie negative Auswirkungen auf die menschliche Gesundheit haben.[3]Regionale Zahlen, die für Italien zum Datum des 12. April verfügbar sind, zeigen, dass etwa 30 % der derzeit positiv getesteten Menschen immer noch in der Lombardei leben (etwa 40 %, wenn man die Gesamtzahl der seit Beginn der Epidemie bestätigten Fälle berücksichtigt), gefolgt von der Emilia Romagna (13,5 %). , Piemont (10,5 %) und Venetien (10 %).[2]Auf diese vier Regionen der Poebene entfallen 80 % aller in Italien verzeichneten Todesfälle und 65 % aller Einweisungen auf Intensivstationen.[2]
Eine von der Harvard School of Public Health durchgeführte Studie scheint einen Zusammenhang zwischen einem Anstieg der PM-Konzentration und der Sterblichkeitsrate aufgrund von COVID-19 in den USA zu bestätigen.[4] In früheren Mitteilungen haben wir die Möglichkeit angenommen, dass SARS-CoV-2 Das Virus könnte während der Ausbreitung der Infektion auf Feinstaub (PM) vorhanden sein,[5,6], was bereits belegt ist
für andere Viren verfügbar.[7-15] Allerdings ist das Problem des in der Luft übertragenen PM-assoziierten Mikrobioms, insbesondere in städtischen Umgebungen, noch weitgehend unzureichend untersucht,[16] und – derzeit hat noch niemand gezielte experimentelle Studien durchgeführt bei der Bestätigung oder dem Ausschluss des Vorhandenseins von SARS-CoV-2 auf PM.
Hier präsentieren wir die ersten Ergebnisse der Analysen, die wir an 34 PM10-Proben von PM10 im Freien/in der Luft von einem Industriestandort in der Provinz Bergamo durchgeführt haben, die mit zwei verschiedenen Luftkeimsammlern über einen kontinuierlichen Zeitraum von drei Wochen vom 21. Februar bis März gesammelt wurden 13.
Nach der von Pan et al. beschriebenen Methodik.Im Jahr 2019 (zur Sammlung, Partikelgrößenbestimmung und Erkennung von in der Luft befindlichen Viren)[17] wurden PM-Proben auf Quarzfaserfiltern mithilfe eines gravimetrischen Luftkeimsammlers mit geringem Volumen (38,3 l/min für 23 Stunden) gemäß der Referenzmethode EN12341 gesammelt :2014 für die PM10-Überwachung.Die Partikel wurden zu durchschnittlich 99,9 % auf den Filtern zurückgehaltenAerosolretention, ordnungsgemäß gelagert und an das Labor für Angewandte und Vergleichende Genomik der Universität Triest geliefert.Angesichts der „Umwelt“-Beschaffenheit der Probe, die vermutlich reich an DNA-Polymerase-Inhibitoren ist, fuhren wir mit der Extraktion von RNA fort, indem wir das Quick RNA-Kit für fäkale Bodenmikroben verwendeten, das an den Typ der Filter angepasst war.[18]Halbfilter wurde gerollt, mit der Oberseite nach innen,in einem 5-ml-Polypropylenröhrchen zusammen mit den im Kit enthaltenen Perlen.Aus dem anfänglichen 1 ml Lysepuffer konnten wir etwa 400 µl Lösung gewinnen, die dann gemäß den Standardprotokollen verarbeitet wurde, was zu einem Endeluat von 15 µl führte.Anschließend wurden 5 µl für den SARS-CoV-2-Test verwendet.Aufgrund der besonderen Herkunft der Probe wurde der qScript XLT 1-Step RT-qPCR ToughMix verwendet.[19]Die Amplifikationssysteme entsprachen dem von Corman et al. entwickelten und auf der WHO-Website veröffentlichten Protokoll [20].
Der Test zielte ausdrücklich darauf ab, das Vorhandensein der SARS-CoV-2-RNA auf Feinstaub zu bestätigen oder auszuschließen.Die erste Analyse verwendete das „E-Gen“ als molekularen Marker und lieferte bei 15 von 16 Filtern ein beeindruckend positives Ergebnis, selbst wenn der Ct erwartungsgemäß zwischen 36 und 38 Zyklen lag.
Danach haben wir die Analyse auf 6 der positiven Filter (bereits positiv auf „E-Gen“) wiederholt, indem wir das „RtDR-Gen“ als molekularen Marker verwendet haben – der hochspezifisch für SARS-CoV-2 ist – und dabei 5 signifikante Ergebnisse erzielt der Positivität;Kontrolltests zum Ausschluss falscher Positivität wurden ebenfalls erfolgreich durchgeführt (Abb. 1).
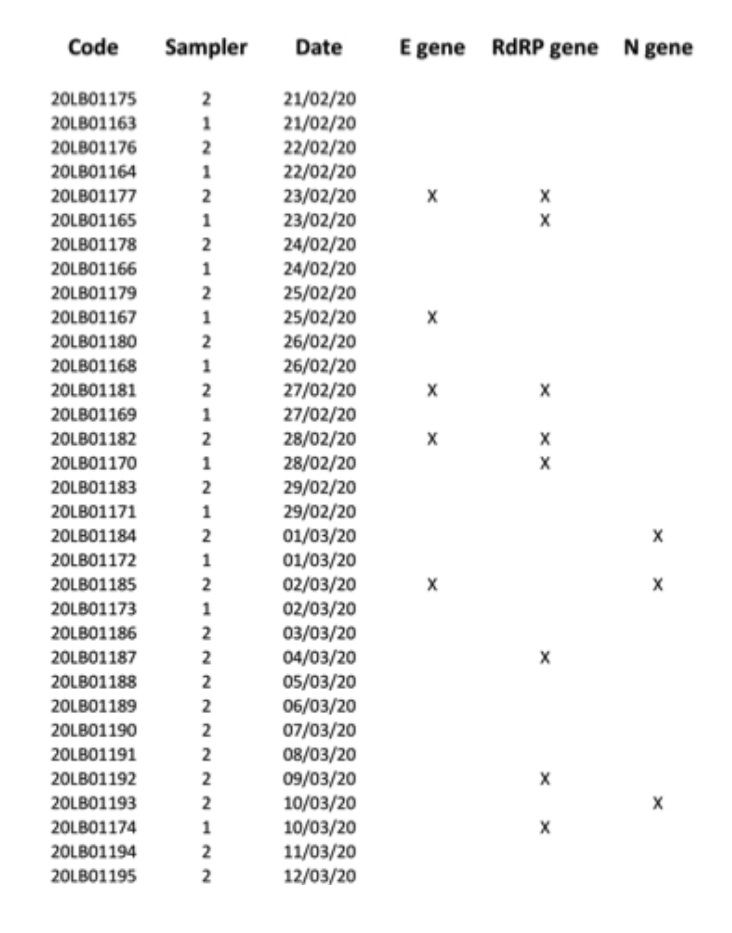
Um zu verhindern, dass das knappe verfügbare Probenmaterial zur Neige geht, wurden die verbleibenden extrahierten RNAs an das örtliche Universitätskrankenhaus (eines der von der italienischen Regierung für SARS-CoV-2-Diagnosetests zugelassenen klinischen Zentren) geliefert, um dort eine zweite durchzuführen paralleler Blindtest.Dieses zweite klinische Labor testete 34 RNA-Extraktionen für die E-, N- und RdRP-Gene und meldete 7 positive Ergebnisse für mindestens eines der drei Markergene, wobei die Positivität für alle drei Marker separat bestätigt wurde (Abb. 2).Aufgrund der Art der Probe und unter Berücksichtigung der Tatsache, dass die Probenahme nicht für klinische Diagnosezwecke, sondern für Umweltverschmutzungstests durchgeführt wurde (unter Berücksichtigung der Tatsache, dass die Filter mindestens vier Wochen lang gelagert wurden, bevor sie molekulargenetischen Analysen unterzogen wurden, z. B(eine Folge des italienischen Shutdowns) können wir bestätigen, dass wir das Vorhandensein von SARS-CoV-2-Virus-RNA durch den Nachweis des hochspezifischen „RtDR-Gens“ auf 8 Filtern hinreichend nachgewiesen haben.Aufgrund des Mangels an zusätzlichen Materialien aus den Filtern konnten wir jedoch nicht genügend Tests wiederholen, um ein positives Ergebnis für alle drei molekularen Marker gleichzeitig zu zeigen.
Dies ist der erste vorläufige Beweis dafür, dass SARS-CoV-2-RNA auf Feinstaub im Freien vorhanden sein kann, was darauf hindeutet, dass SARS-CoV-2 unter Bedingungen atmosphärischer Stabilität und hoher Feinstaubkonzentration Cluster mit Feinstaub im Freien bilden könnte Verringerung ihres Diffusionskoeffizienten – Verbesserung der Persistenz des Virus in der Atmosphäre.Weitere Bestätigungen dieser vorläufigenDie entsprechenden Beweise sind noch im Gange und sollten eine Echtzeitbewertung der Vitalität von SARS-CoV-2 sowie seiner Virulenz bei Adsorption an Feinstaub umfassen.Derzeit können keine Annahmen über den Zusammenhang zwischen dem Vorhandensein des Virus auf PM und dem Verlauf des COVID-19-Ausbruchs getroffen werden.Weitere Probleme, die speziell angegangen werden müssen, sind die durchschnittlichen PM-KonzentrationenDies ist für einen potenziellen „Boost-Effekt“ der Ansteckung erforderlich (falls bestätigt wird, dass PM als „Träger“ für die viralen Tröpfchenkerne fungieren könnte) oder sogar für die theoretische Möglichkeit einer Immunisierung infolge minimaler Dosenexpositionen bei niedrigeren PM-Schwellenwerten .
Abb.1 Amplifikationskurven der E- (A) und RdRP-Gene (B): grüne Linien stellen getestete Filter dar;Kreuzlinienstellt Referenzfilterextraktionen dar;Rote Linien stellen die Amplifikation der positiven Proben dar.
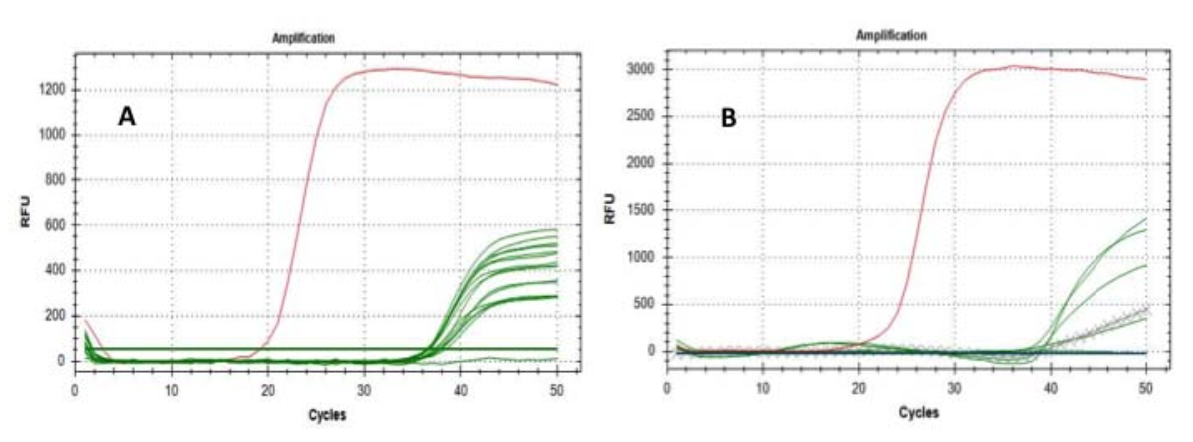
Abb.2.Positive Ergebnisse (mit X markiert) für E-, N- und RdRP-Gene, die für alle 34 PM10-Proben erhalten wurdenFilter, die in den zweiten Parallelanalysen getestet wurden.
 Leonardo Setti1, Fabrizio Passarini2, Gianluigi De Gennaro3, Pierluigi Barbieri4, Maria Grazia Perrone5, Massimo Borelli6, Jolanda Palmisani3, Alessia Di Gilio3, Valentina Torboli6, Alberto Pallavicini6, Maurizio Ruscio7, Prisco Piscitelli8, Alessandro Miani8,9
Leonardo Setti1, Fabrizio Passarini2, Gianluigi De Gennaro3, Pierluigi Barbieri4, Maria Grazia Perrone5, Massimo Borelli6, Jolanda Palmisani3, Alessia Di Gilio3, Valentina Torboli6, Alberto Pallavicini6, Maurizio Ruscio7, Prisco Piscitelli8, Alessandro Miani8,9
1. Abteilung für Industrielle Chemie, Universität Bologna, Viale del Risorgimento – 4, I-40136, Bologna, Italien
e-mail: leonardo.setti@unibo.it
2. Interdepartementales Zentrum für Industrieforschung „Erneuerbare Quellen, Umwelt, blaues Wachstum, Energie“,
University of Bologna, Rimini, Italy e-mail: fabrizio.passarini@unibo.it
3. Fakultät für Biologie, Universität „Aldo Moro“ von Bari, Bari, Italien
e-mail: gianluigi.degennaro@uniba.it; alessia.digilio@uniba.it; jolanda.palmisani@uniba.it
4. Fakultät für Chemische und Pharmazeutische Wissenschaften, Universität Triest, Triest, Italien
e-mail: barbierp@units.it
5. Abteilung für Umweltforschung, TCR TECORA, Mailand, Italien
e-mail: mariagrazia.perrone@tcrtecora.com
6. Fakultät für Biowissenschaften – Universität Triest, Triest, Italien
e-mail: borelli@units.it; torboli@units.it; pallavic@units.it
7. Abteilung für Labormedizin, Universitätsklinikum Giuliano Isontina (ASU GI), Triest, Italien
email: maurizio.ruscio@asugi.sanita.fvg.it
8. Italienische Gesellschaft für Umweltmedizin (SIMA), Mailand, Italien
e-mail: priscofreedom@hotmail.com; alessandro.miani@unimi.it
9. Institut für Umweltwissenschaften und Politik, Universität Mailand, Mailand, Italien
e-mail: priscofreedom@hotmail.com; alessandro.miani@unimi.it
Korrespondierender Autor:
Leonardo Setti, Department of Industrial Chemistry, University of Bologna Viale del Risorgimento 4, 40136, Bologna, Italy; e-mail: leonardo.setti@unibo.it
Verweise
1. Weltgesundheitsorganisation, Übertragungswege des Virus, der COVID-19 verursacht: Auswirkungen auf die Vorsichtsmaßnahmenempfehlungen des IPC, Wissenschaftlicher Bericht;verfügbar unter: https://www.who.int/newsroom/commentaries/detail/modes-of-transmission-of-virus-causing-covid-19-implications-for-ipcprecaution-recommendations (29. März 2020)
2. Italienisches Gesundheitsministerium, tägliches Bulletin Covid-19-Ausbruch in Italien, verfügbar unter http://www.salute.gov.it/imgs/C_17_notizie_4451_0_file.pdf
3. EUA, Europäische Umweltagentur, Bericht zur Luftqualität in Europa 2019;Nr. 10/2019;Europäische Umweltagentur: Kopenhagen, Dänemark, verfügbar unter: https://www.eea.europa.eu/publications/airquality-in-europe-2019
4. Xiao Wu, Rachel C. Nethery, M. Benjamin Sabath, Danielle Braun, Francesca Dominici, Exposition gegenüber Luftverschmutzung und COVID-19-Mortalität in den Vereinigten Staaten, verfügbar unter: https://projects.iq.harvard.edu/ files/covid-pm/files/pm_and_covid_mortality.pdf
5. Italienische Gesellschaft für Umweltmedizin (SIMA), Positionspapier Feinstaub und COVID-19,
verfügbar unter: http://www.simaonlus.it/wpsima/wp-content/uploads/2020/03/COVID_19_positionpaper_ENG.pdf
6. Setti L., Passarini F., De Gennaro G., Barbieri P., Perrone MG, Piazzalunga A., Borelli M., Palmisani J., Di Gilio A, Piscitelli P, Miani A., Gibt es eine plausible Rolle? for Particulate Matter in the spreading of COVID-19 in Northern Italy?, BMJ Rapid Responses, 8. April 2020, verfügbar unter: https://www.bmj.com/content/368/bmj.m1103/rapid-responses
7. Sedlmaier, N., Hoppenheidt, K., Krist, H., Lehmann, S., Lang, H., Buttner, M. Entstehung von mit dem Vogelgrippevirus (AIV) kontaminiertem fäkalem Feinstaub (PM2,5): Genom- und Infektiositätserkennung und Immissionsberechnung.Veterinärmikrobiologie.139, 156-164 (2009)
8. Zhao, Y., Richardson, B., Takle, E., Chai, L., Schmitt, D., Win, H. Die Übertragung über die Luft könnte eine Rolle bei der Ausbreitung der hochpathogenen Vogelgrippe-Ausbrüche im Jahr 2015 gespielt haben Vereinigte Staaten.Sci Rep. 9, 11755. https://doi.org/10.1038/s41598-019-47788-z (2019)
9. Ma, Y., Zhou, J., Yang, S., Zhao, Y., Zheng, X. Bewertung der Auswirkungen von Staubereignissen auf die Maserninzidenz in Westchina.Atmosphärische Umgebung.157, 1-9 (2017)
10. Sorensen, JH, Mackay, DKJ, Jensen, C. Ø., Donaldson, AI Ein integriertes Modell zur Vorhersage der atmosphärischen Ausbreitung des Maul- und Klauenseuchevirus Epidemiol.Infect., 124, 577–590 (2000)
11. Glostera, J., Alexandersen, S. New Directions: Airborne Transmission of Foot-and-Mouth Disease Virus Atmospheric Environment, 38 (3), 503-505 (2004)
12. Reche, I., D'Orta, G., Mladenov, N., Winget, DM, Suttle, CA Ablagerungsraten von Viren und Bakterien über der atmosphärischen Grenzschicht.Das ISME Journal.12, 1154-1162 (2018)
13. Qin, N., Liang, P., Wu, C., Wang, G., Xu, Q., Xiong, X., Wang, T., Zolfo, M., Segata, N., Qin, H ., Knight, R., Gilbert, JA, Zhu, TF Längsschnittuntersuchung des Mikrobioms im Zusammenhang mit Feinstaub in einer Megacity.Genombiologie.21, 55 (2020)
14. Zhao, Y., Richardson, B., Takle, E., Chai, L., Schmitt, D., Win, H. Übertragung durch die Luft kann möglich sein
spielte eine Rolle bei der Ausbreitung der hochpathogenen Vogelgrippe-Ausbrüche im Jahr 2015 in den Vereinigten Staaten.Wissenschaft
Rep. 9, 11755. https://doi.org/10.1038/s41598-019-47788-z (2019)
15. Ma, Y., Zhou, J., Yang, S., Zhao, Y., Zheng, X. Bewertung der Auswirkungen von Staubereignissen auf die Maserninzidenz in Westchina.Atmosphärische Umgebung.157, 1-9 (2017)
16. Jiang, W., Laing, P., Wang, B., Fang, J., Lang, J., Tian, G., Jiang, J., Zhu, TF Optimierte DNA-Extraktion und metagenomische Sequenzierung von mikrobiellen Gemeinschaften in der Luft .Nat.Protokoll.10, 768-779 (2015)
17. Pan, M., Lednicky, JA, Wu, C.-Y., Sammlung, Partikelgröße und Nachweis von durch die Luft übertragenen Viren.Journal of Applied Microbiology, 127, 1596-1611 (2019)
18. Zymoresearch Ldt, Produktbeschreibung, verfügbar unter: https://www.zymoresearch.com/products/quick-rnafecal-soil-microbe microprep-kit
19. Quantabio Ltd, Beschreibung des Produkts, verfügbar unter: https://www.quantabio.com/qscript-xlt-1-steprt-qpcr-toughmix
20. Corman, VM, Landt, O., Kaiser, M., Molenkamp, R., Meijer, A., Chu, DK und Mulders, DG (2020).
Nachweis des neuartigen Coronavirus 2019 (2019-nCoV) mittels Echtzeit-RT-PCR.Eurosurveillance, 25(3), verfügbar unter: https://www.ncbi.nlm.nih.gov/pmc/articles/PMC6988269/
Original: https://doi.org/10.1101/2020.04.15.20065995
Zeitpunkt der Veröffentlichung: 18. April 2020
